Zytogenetische Diagnostik
Leitung: Dr. rer. nat. Jutta Dietzel-Dahmen
E-Mail: jutta.dietzel-dahmen@uni-duesseldorf.de
Telefon: 0211/81-06786
Technische Mitarbeiterinnen: Angelika Krebs-Roszyk
Telefon: 0211/81-05128
Chromosomenanalyse
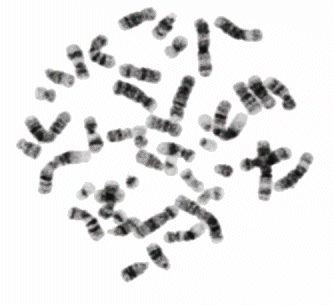
Bei der Chromosomenanalyse werden die Chromosomen, die Träger der Erbinformation, im Mikroskop sichtbar gemacht und untersucht. Bei dieser Untersuchung wird der gesamte Chromosomensatz des Menschen dargestellt. Die Chromosomen isoliert man aus sich teilenden Zellen. Deshalb werden die Zellen zunächst in einer Zellkultur gepflegt und vermehrt, bis ausreichend teilungsfähige Zellen zur Verfügung stehen. Nach der Präparation der Chromosomen werden diese auf den Objektträgern „gebändert“ und können dann im Lichtmikroskop numerisch und strukturell analysiert werden.
Eine strukturelle Analyse umfasst den Vergleich der Lage des Zentromers und der für jedes Chromosom spezifischen Abfolge von Banden. Dadurch können beispielsweise Inversionen, Translokationen, Duplikationen oder Deletionen einzelner Chromosomen nachgewiesen werden. Die numerische Analyse erfasst Abweichungen von der normalen Chromosomenanzahl (wie z. B. Trisomien).
Postnatale Diagnostik:
Untersuchungsmaterial:
- heparinisiertes Venenblut
- Fibroblasten
- Mundschleimhautzellen (nach Rücksprache)
Indikationen (Auswahl):
Kinder:
- Geistige oder körperliche Entwicklungsstörung
- Syndromverdacht (Dysmorphiezeichen, Fehlbildungen)
- Wachstumsauffälligkeiten
(bei ca. 0,5% aller lebend geborenen Kinder treten Chromosomenveränderungen auf)
Erwachsene:
- Familiäre Chromosomenstörung
- Kleinwuchs / Großwuchs
- Habituelle Aborte
- Sterilität, Fertilitätsstörungen
- Kind mit nachgewiesener oder vermuteter Chromosomenveränderung
Methodisches Spektrum:
Konventionelle zytogenetische Analyse :
- Zellkultur
- Präparation von Metaphasechromosomen
- GTG-Banding, (CBG-Banding, QFQ-Banding, NOR-Färbung nach Bedarf)
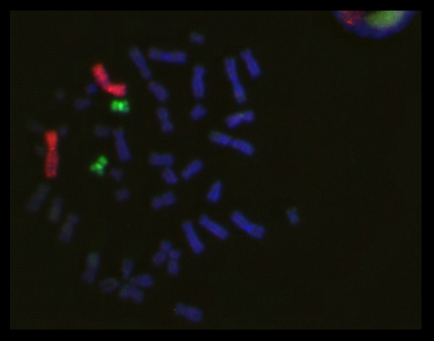
Molekularzytogentische Analysen (Fluoreszenz-in-situ-Hybridisierung, FISH):
Die FISH-Technik beruht auf der Hybridisierung von DNA-Sonden, die spezifische chromosomale Strukturen identifizieren. Es können Sonden verwendet werden, die spezifisch die Zentromer-Region einzelner Chromosomen, Gene oder ganze Chromosomen markieren. Die DNA der eingesetzten Sonden und die zu untersuchende Patienten-DNA werden denaturiert, d.h. die beiden DNA-Stränge der Doppelhelix werden getrennt. Bei der anschließenden Renaturierung lagern sich die DNA-Sonden an die komplementären Abschnitte der Patienten-DNA an (Hybridisierung). Die DNA-Sonden sind entweder direkt mit einem Fluoreszenz-Farbstoff markiert oder werden mit Hilfe von fluoreszenzgekoppelten Antikörpern nachgewiesen. Die entsprechenden Chromosomenstrukturen sind somit als Fluoreszenz-Signale auswertbar.
Ein großer Vorteil dieser Methode ist, dass sie nicht nur an Metaphasen sondern auch an Interphase-Kernen durchgeführt werden kann. Ein Nachteil ist, dass man nur Informationen über die Chromosomen/Gene erhält, für die die Sonden eingesetzt wurden.
- Gesamtchromosom-spezifische Sonden (Abklärung chromosomaler Rearrangements)
- Zentromersonden (numerische Aberrationen der Gonosomen)
- Mikrodeletionssyndrome: DiGeorge-Syndrom, Williams-Beuren-Syndrom, andere nach vorheriger Absprache
- Interphasen-FISH an Mundschleimhautzellen bei V. a. Vorliegen eines Mosaikes
Materialentnahme und Versand:
≥2 ml Vollblut (bei Säuglingen und Kleinkindern ggf. auch weniger) in Li-Heparin-Monovetten aufziehen. Versand über den normalen Postweg.
Methodisches Spektrum:
Konventionelle zytogenetische Analyse:
- Zellkultur
- Präparation von Metaphasechromosomen
- GTG-Banding, (CBG-Banding, QFQ-Banding, NOR-Färbung nach Bedarf)
- computergestützte Karyotypisierung


